SABNP & Synsight : Intégrer informatique, biologie structurale et exploration in vivo pour découvrir de nouveaux médicaments
Source(s): Genopole
SABNP et Synsight valident une approche intégrée de découverte de nouveaux médicaments, alliant informatique, biologie structurale et exploration in vivo.
Deux acteurs du biocluster Genopole, le laboratoire SABNP (Université d’Évry Paris-Saclay) et la startup Synsight, ont développé une approche intégrée de criblage de nouveaux médicaments qui s’appuie à la fois sur la modélisation informatique, l’analyse structurale des molécules biologiques et une technologie brevetée d’étude des interactions protéines-ARN au sein même de la cellule.
La démarche des scientifiques génopolitains cible des pistes thérapeutiques modulant ou inhibant ces interactions, prometteuses pour des cancers et diverses maladies, dont la découverte était jusque-là freinée par le manque de méthodes.
Dans un organisme vivant, la liaison entre protéines et molécules d’ARN, ARN messager codant pour d’autres protéines ou ARN non codant aux divers rôles biologiques, est un phénomène essentiel au fonctionnement de chaque cellule et de l’organisme tout entier. Le génome humain code par exemple pour plus de 1 000 protéines de cette nature. Les liaisons protéines-ARN régulent notamment l’expression de nos gènes. Elles sont parfois la cause de pathologies, par exemple de maladies neurodégénératives et de cancers.
Une classe méconnue de nouveaux médicaments
Cibler les interactions protéine-ARN est une voie prometteuse pour la découverte de nouveaux médicaments. Cette piste thérapeutique est jusqu’à présent largement sous-exploitée car elle se heurte à deux obstacles : d’une part le manque de modèles informatiques pour un criblage in silico de composés ciblant la poche moléculaire, siège de l’interaction, et d’autre part la difficulté de détecter expérimentalement, dans la cellule, ces interactions.
Le laboratoire SABNP, dirigé par David Pastré et sous tutelle de l’Université d’Évry Paris-Saclay, et la société Synsight, fondée par Cyril Bauvais, ont conçu une approche de criblage thérapeutique exploitant des données chimiques, structurales et cellulaires.
Elle combine trois types de méthodes :
- des modèles computationnels pour prédire à grande échelle, sur des millions de molécules, l’aptitude à se lier à la poche moléculaire cible, et intégrer leurs caractéristiques d’absorption, distribution, toxicité et autres propriétés physico-chimiques utiles pour les sélectionner sur leur potentiel à devenir des médicaments.
- l’expertise en biologie structurale du laboratoire, notamment l’exploration 3D de la poche cible et l’analyse par spectroscopie de résonance magnétique nucléaire (RMN) de la liaison des molécules candidates à cette poche.
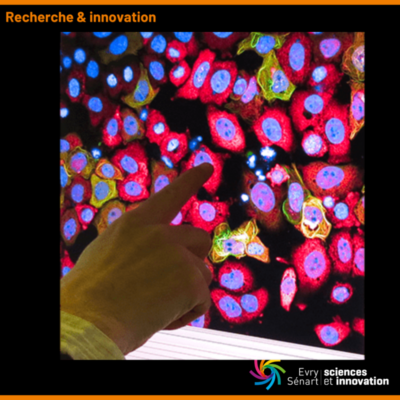
- la méthode Microtubule bench (MT bench), brevetée par SABNP, qui utilise une structure cellulaire naturelle, les microtubules, pour observer dans la cellule les interactions entre protéines, ou entre protéines et ARN (cf. photo). Associée à un imageur HCS (high content screening), équipement de très haute résolution acquis grâce au soutien de Genopole et l’Université d’Evry, et à l’analyse automatique d’image, cette plateforme de test in vivo visualise et quantifie ces interactions.
En conclusion
Les scientifiques de SABNP et Synsight ont validé leur approche intégrée : ils ont démontré l’efficacité du test MT bench, unique au monde, en complément des méthodes de prédictions informatiques et de l’analyse structurale fine, pour identifier des candidats médicaments ciblant l’interaction entre la protéine YB-1 et l’ARN messager.
Ils projettent de confirmer le succès de l’approche en étendant leurs recherches à d’autres liaisons protéines – ARN, ou de cibler des interactions entre protéine et ARN spécifiques, par exemple ARN codant pour un gène particulier ou ARN non codant gouvernant un mécanisme biologique précis, ciblant ainsi une certaine maladie.
